Nat Med | Isang multi-omics na pamamaraan sa pagmamapa ng pinagsamang tumor, immune, at microbial na tanawin ng colorectal cancer ang nagpapakita ng interaksyon ng microbiome sa immune system.
Bagama't malawakang pinag-aralan ang mga biomarker para sa primary colon cancer nitong mga nakaraang taon, ang kasalukuyang mga klinikal na alituntunin ay umaasa lamang sa staging ng tumor-lymph node-metastasis at pagtuklas ng mga depekto sa DNA mismatch repair (MMR) o microsatellite instability (MSI) (bilang karagdagan sa karaniwang pagsusuri sa patolohiya) upang matukoy ang mga rekomendasyon sa paggamot. Napansin ng mga mananaliksik ang kakulangan ng kaugnayan sa pagitan ng mga tugon ng immune system batay sa gene expression, mga microbial profile, at tumor stroma sa Cancer Genome Atlas (TCGA) colorectal cancer cohort at kaligtasan ng pasyente.
Habang umuunlad ang pananaliksik, ang mga quantitative na katangian ng primary colorectal cancer, kabilang ang cancer cellular, immune, stromal, o microbial na katangian ng kanser, ay naiulat na may makabuluhang kaugnayan sa mga klinikal na resulta, ngunit limitado pa rin ang pag-unawa kung paano nakakaapekto ang kanilang mga interaksyon sa mga resulta ng pasyente.
Upang masuri ang ugnayan sa pagitan ng phenotypic complexity at kinalabasan, isang pangkat ng mga mananaliksik mula sa Sidra Institute of Medical Research sa Qatar ang kamakailang bumuo at nagpatunay ng isang integrated score (mICRoScore) na tumutukoy sa isang grupo ng mga pasyente na may mahusay na survival rate sa pamamagitan ng pagsasama-sama ng mga katangian ng microbiome at immune rejection constants (ICR). Ang pangkat ay nagsagawa ng isang komprehensibong genomic analysis ng mga sariwang frozen sample mula sa 348 pasyente na may primary colorectal cancer, kabilang ang RNA sequencing ng mga tumor at katugmang malusog na colorectal tissue, whole exome sequencing, deep T-cell receptor at 16S bacterial rRNA gene sequencing, na dinagdagan ng whole tumor genome sequencing upang higit pang makilala ang microbiome. Ang pag-aaral ay inilathala sa Nature Medicine bilang "An integrated tumor, immune and microbiome atlas of colon cancer".

Artikulo na inilathala sa Nature Medicine
Pangkalahatang-ideya ng AC-ICAM
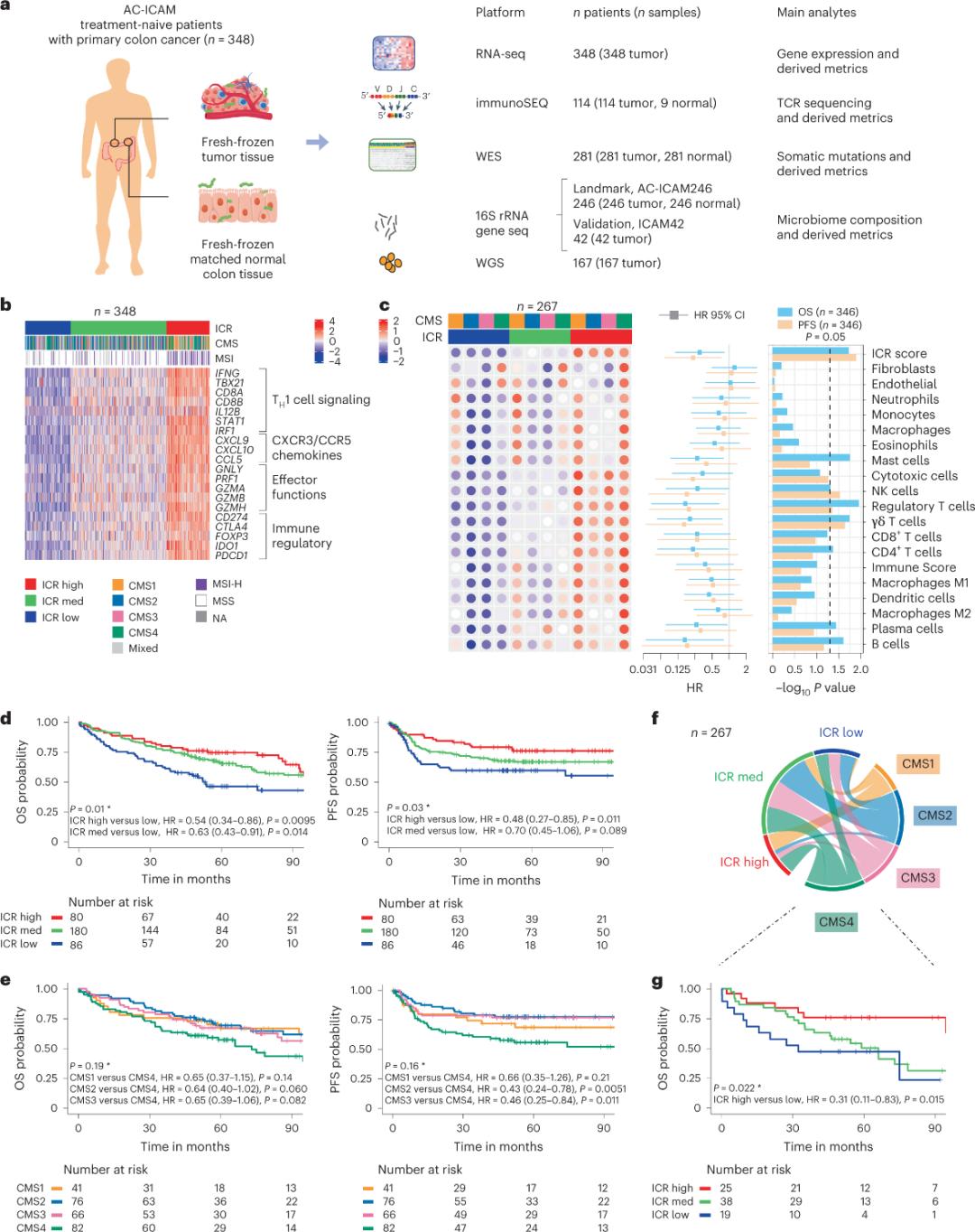
Gumamit ang mga mananaliksik ng isang orthogonal genomic platform upang suriin ang mga sariwang nakapirming sample ng tumor at itinugma ang katabing malusog na tisyu ng colon (mga pares ng tumor-normal) mula sa mga pasyenteng may histologic diagnosis ng kanser sa colon nang walang systemic therapy. Batay sa whole-exome sequencing (WES), RNA-seq data quality control, at inclusion criteria screening, ang genomic data mula sa 348 pasyente ay pinanatili at ginamit para sa downstream analysis na may median follow-up na 4.6 na taon. Pinangalanan ng research team ang resource na ito na Sidra-LUMC AC-ICAM: A map and guide to immune-cancer-microbiome interactions (Figure 1).
Pag-uuri ng molekula gamit ang ICR
Gamit ang isang modular set ng immune genetic markers para sa continuous cancer immunosurveillance, na tinatawag na immune constant of rejection (ICR), in-optimize ng research team ang ICR sa pamamagitan ng pagpapaikli nito sa isang 20-gene panel na sumasaklaw sa iba't ibang uri ng kanser, kabilang ang melanoma, kanser sa pantog, at kanser sa suso. Ang ICR ay naiugnay din sa tugon ng immunotherapy sa iba't ibang uri ng kanser, kabilang ang kanser sa suso.
Una, pinatunayan ng mga mananaliksik ang ICR signature ng AC-ICAM cohort, gamit ang isang ICR gene-based co-classification approach upang uriin ang cohort sa tatlong cluster/immune subtypes: high ICR (hot tumors), medium ICR at low ICR (cold tumors) (Figure 1b). Inilarawan ng mga mananaliksik ang immune propensity na nauugnay sa consensus molecular subtypes (CMS), isang transcriptome-based na klasipikasyon ng colon cancer. Kasama sa mga kategorya ng CMS ang CMS1/immune, CMS2/canonical, CMS3/metabolic at CMS4/mesenchymal. Ipinakita ng pagsusuri na ang mga ICR score ay negatibong nauugnay sa ilang pathway ng cancer cell sa lahat ng CMS subtypes, at ang mga positibong ugnayan sa mga immunosuppressive at stromal-related pathways ay naobserbahan lamang sa mga tumor ng CMS4.
Sa lahat ng CMS, ang kasaganaan ng natural killer (NK) cell at T cell subsets ay pinakamataas sa mga ICR high immune subtypes, na may mas malaking pagkakaiba-iba sa iba pang mga leukocyte subsets (Figure 1c). Ang mga ICR immune subtypes ay may iba't ibang OS at PFS, na may progresibong pagtaas sa ICR mula mababa hanggang mataas (Figure 1d), na nagpapatunay sa prognostic role ng ICR sa colorectal cancer.
Pigura 1. Disenyo ng pag-aaral ng AC-ICAM, lagda ng gene na may kaugnayan sa immune system, mga subtype ng immune system at molekular, at kaligtasan.
Kinukuha ng ICR ang mga tumor-enriched, clonally amplified T cells
Iilang T cell lamang na pumapasok sa tisyu ng tumor ang naiulat na espesipiko para sa mga tumor antigen (mas mababa sa 10%). Samakatuwid, ang karamihan sa mga intra-tumor T cell ay tinutukoy bilang bystander T cells (bystander T cells). Ang pinakamalakas na ugnayan sa bilang ng mga conventional T cells na may mga produktibong TCR ay naobserbahan sa mga subpopulasyon ng stromal cell at leukocyte (natukoy ng RNA-seq), na maaaring gamitin upang tantyahin ang mga subpopulasyon ng T cell (Larawan 2a). Sa mga kumpol ng ICR (pangkalahatan at klasipikasyon ng CMS), ang pinakamataas na clonality ng immune SEQ TCRs ay naobserbahan sa mga grupong may ICR-high at CMS subtype CMS1/immune (Larawan 2c), na may pinakamataas na proporsyon ng mga tumor na may ICR-high. Gamit ang buong transcriptome (18,270 genes), anim na ICR genes (IFNG, STAT1, IRF1, CCL5, GZMA, at CXCL10) ang kabilang sa nangungunang sampung genes na positibong nauugnay sa clonality ng TCR immune SEQ (Larawan 2d). Ang clonality ng ImmunoSEQ TCR ay mas malakas na nauugnay sa karamihan ng mga gene ng ICR kaysa sa mga ugnayan na naobserbahan gamit ang mga marker ng CD8+ na tumutugon sa tumor (Larawan 2f at 2g). Bilang konklusyon, ang pagsusuri sa itaas ay nagmumungkahi na ang ICR signature ay kumukuha ng presensya ng mga tumor-enriched, clonally amplified T cell at maaaring ipaliwanag ang mga prognostic na implikasyon nito.
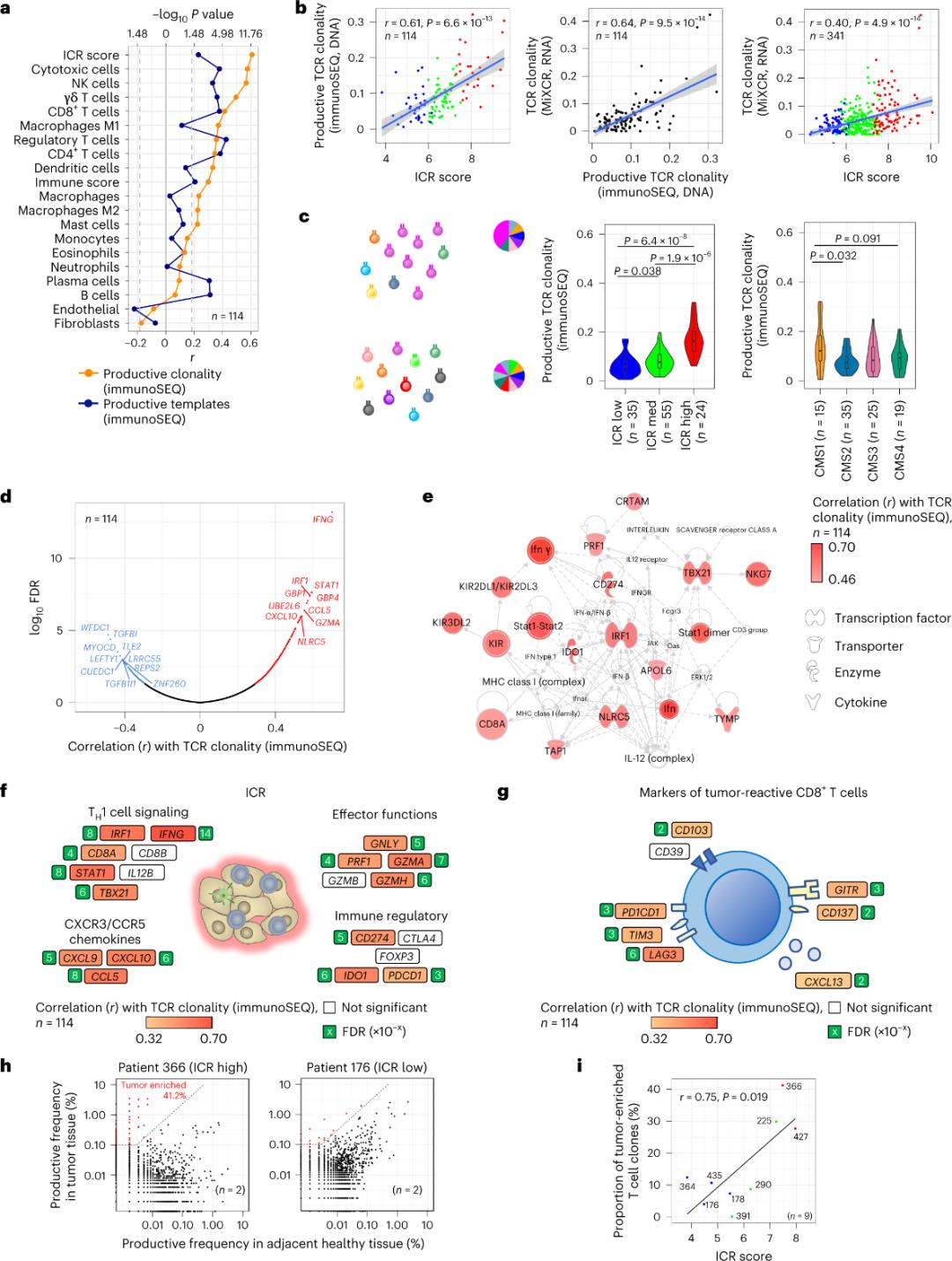
Pigura 2. Mga sukatan ng TCR at ugnayan sa mga gene na may kaugnayan sa immune system, immune system at molekular na mga subtype.
Komposisyon ng microbiome sa malusog at mga tisyu ng kanser sa colon
Isinagawa ng mga mananaliksik ang 16S rRNA sequencing gamit ang DNA na kinuha mula sa magkatugmang tumor at malusog na tisyu ng colon mula sa 246 na pasyente (Larawan 3a). Para sa pagpapatunay, sinuri rin ng mga mananaliksik ang datos ng 16S rRNA gene sequencing mula sa karagdagang 42 sample ng tumor na walang tugmang normal na DNA na magagamit para sa pagsusuri. Una, inihambing ng mga mananaliksik ang relatibong kasaganaan ng flora sa pagitan ng magkatugmang tumor at malusog na tisyu ng colon. Ang Clostridium perfringens ay tumaas nang malaki sa mga tumor kumpara sa malulusog na sample (Larawan 3a-3d). Walang makabuluhang pagkakaiba sa alpha diversity (pagkakaiba-iba at kasaganaan ng mga species sa isang sample) sa pagitan ng tumor at malulusog na sample, at isang katamtamang pagbawas sa microbial diversity ang naobserbahan sa mga tumor na may ICR na mataas kumpara sa mga tumor na may ICR na mababa.
Upang matukoy ang mga klinikal na kaugnay na kaugnayan sa pagitan ng mga profile ng mikrobyo at mga klinikal na kinalabasan, nilayon ng mga mananaliksik na gamitin ang datos ng 16S rRNA gene sequencing upang matukoy ang mga katangian ng microbiome na humuhula sa kaligtasan. Sa AC-ICAM246, nagpatakbo ang mga mananaliksik ng isang modelo ng OS Cox regression na pumili ng 41 katangian na may mga non-zero coefficients (na nauugnay sa differential mortality risk), na tinatawag na MBR classifiers (Figure 3f).
Sa training cohort na ito (ICAM246), ang mababang MBR score (MBR<0, mababang MBR) ay nauugnay sa mas mababang panganib ng kamatayan (85%). Kinumpirma ng mga mananaliksik ang kaugnayan sa pagitan ng mababang MBR (panganib) at matagal na OS sa dalawang magkahiwalay na napatunayang cohort (ICAM42 at TCGA-COAD). (Larawan 3) Ang pag-aaral ay nagpakita ng isang malakas na ugnayan sa pagitan ng endogastric cocci at mga marka ng MBR, na magkatulad sa tumor at malusog na tisyu ng colon.
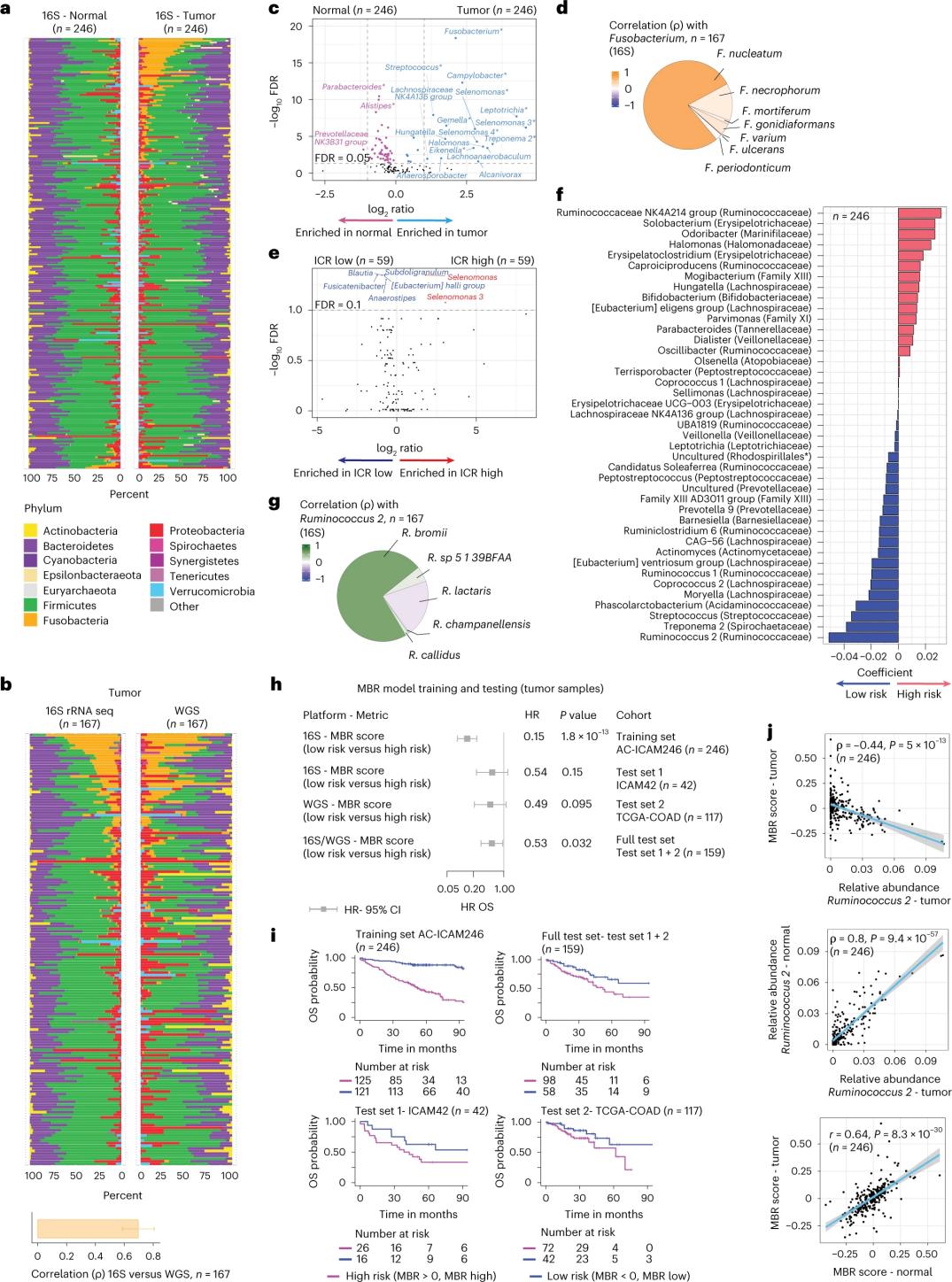
Pigura 3. Microbiome sa tumor at malulusog na tisyu at ang kaugnayan sa ICR at kaligtasan ng pasyente.
Konklusyon
Ang pamamaraang multi-omics na ginamit sa pag-aaral na ito ay nagbibigay-daan sa masusing pagtuklas at pagsusuri ng molecular signature ng immune response sa colorectal cancer at nagpapakita ng interaksyon sa pagitan ng microbiome at ng immune system. Ang malalim na TCR sequencing ng tumor at malulusog na tisyu ay nagpapakita na ang prognostic effect ng ICR ay maaaring dahil sa kakayahan nitong makuha ang mga tumor-enriched at posibleng tumor antigen-specific T cell clones.
Sa pamamagitan ng pagsusuri ng komposisyon ng microbiome ng tumor gamit ang 16S rRNA gene sequencing sa mga sample ng AC-ICAM, natukoy ng pangkat ang isang microbiome signature (MBR risk score) na may malakas na prognostic value. Bagama't ang signature na ito ay nagmula sa mga sample ng tumor, mayroong isang malakas na ugnayan sa pagitan ng malusog na colorectum at tumor MBR risk score, na nagmumungkahi na ang signature na ito ay maaaring makuha ang komposisyon ng gut microbiome ng mga pasyente. Sa pamamagitan ng pagsasama-sama ng mga marka ng ICR at MBR, posible na matukoy at mapatunayan ang isang multi-omic student biomarker na humuhula ng kaligtasan ng buhay sa mga pasyenteng may kanser sa colon. Ang multi-omic dataset ng pag-aaral ay nagbibigay ng isang mapagkukunan upang mas maunawaan ang biology ng kanser sa colon at makatulong na matuklasan ang mga isinapersonal na therapeutic approach.
Oras ng pag-post: Hunyo-15-2023
 中文网站
中文网站